周晓北
职称:副教授
联系电话:13998326059
E-mail: xbzhou@cmu.edu.cn
研究领域:生物信息学
周晓北 副教授,研究生导师。
在瑞士苏黎世大学疾获得病防治与生物统计学博士学位,并于2018底通过高层次人才招聘计划入职中国医科大学。现任职中国医科大学健康科学研究院副教授、研究生导师。以生物信息学为研究领域,侧重研究机器学习技术在健康医疗大数据领域的应用和高通量基因测序技术新算法与工具;具有生物医学/临床数据分析能力和经验,可以为各大研究中心提供数据分析、培训和咨询等相关服务。
目前主要研究方向
1. 人工智能在生物医学与健康管理领域的应用。
通过图像识别、深度学习、神经网络等关键技术开发“人工智能+医疗/健康管理”辅助诊疗及健康管理工具。

(目前研发的基于地理人工智能健康环境社区诊断工具开发。(a) 沈阳某社区的卫星高清图片,(b) 通过Satellite-Segmentation模型识别社区中绿植和 (c) 通过VGG16模型识别图片中的人物。)
2. 生物医学数据整合与挖掘和生物学数据库构建。
① PubMed文本挖掘 (https://github.com/xizhou/pubMR)。
②转录组数据整合分析 ()。
③中药网络药理学分析以及新型中药数据库的构建。
3. 基因组学算法
高通量测序数据数据的处理与分析方法。

(edgeR是本人参与研发的R/Bioconductor基因测序分析软件程序包。)
代表性论文
[1] Zhou Xiaobei, Lindsay Henlen, Robinson Mark D. Robustly detecting differential expression in RNA sequencing data using observation weights, Nucleic Acids Research, 2014, 42(11): e91. (IF 11.561)
[2] Zhou Xiaobei, Robinson Mark D. Do count-based differential expression methods perform poorly when genes are expressed in only one condition? Genome Biology, 2015, 16(222), DOI:10.1186/s13059-015-0781-3. (IF 13.214)
[3] Zhou Xiaobei, Oshlack Alicia, Mark D. MiRNA-Seq normalization comparisons need improvement, RNA Journal, 2013, 19(6): 733–734. (IF 4.49)
[4] Robinson Mark D, Kahraman Abdullah, Law Charity W, Lindsay Helen, Malgorzata Nowicka, Weber Lukas M, Zhou Xiaobei. Statistical methods for detecting differentially methylated loci and regions, Frontiers in Genetics, 2014, 5(324), DOI:10.3389/fgene.2014.00324. (IF 4.151)
[5] Littringer Katharina, Moresi Claudia, Rakebrandt Nikolas, Zhou Xiaobei, Schorer Michelle, Dolowschiak Tamas, Kirchner Florian, Rost Felix, Keller Christian W, McHugh Donal, Leibund Gut-Landmann Salome, Robinson Mark D, Joller Nicole. Common features of regulatory T cell specialization during Th1 responses. Frontiers in Immunology, 2018, 9(1344), DOI: 10.3389/fimmu.2018.01344. (IF 5.511)

刘文粟
职称:副研究员
联系电话:18941639110
Email: wliu2019@163.com
研究方向:转录组大数据整合与智慧图谱
2011年美国圣路易斯大学获得硕士学位,2017年中国科学院生物物理所获得博士学位,中国科学院工作半年后,作为师资博士后入中国医科大学生科院博士后流动站,2019年博后出站并入职健康科学研究院。研究方向为基于机器学习的转录组大数据在肿瘤学和脑研究的应用以及智慧图谱的构建。共发表SCI第一作者论文4篇,其中Cell Stem Cell的IF:23.497,Protein & Cell论文两篇。主持在研课题共4项,国家自然科学基金青年基金1项,中国博士后科学基金1项,中国医科大学健康大数据课题1项,博士后启动基金1项。
科研方向:
(1)从事转录组大数据的数据整合和拟合算法的开发,目标是使转录组大数据的精度和信息量接近单细胞测序的水准,并克服单细胞测序偏向性的缺点。并且通过数据整合,挖掘数据中的重要信息,尤其是研究对象的特异性基因。
(2)从事智慧图谱算法的开发,目标是寻找目标因子和重要研究对象的驱动性因子、不同研究对象之间的重要中间因子以及不同因子之间的因果关联,进而为实验验证的方法以及方向提供指导。
(3)从事ncbi等数据库的文本和图形的信息挖掘的算法开发工作,以寻找隐藏在数据库中重要信息。
主要学术贡献:
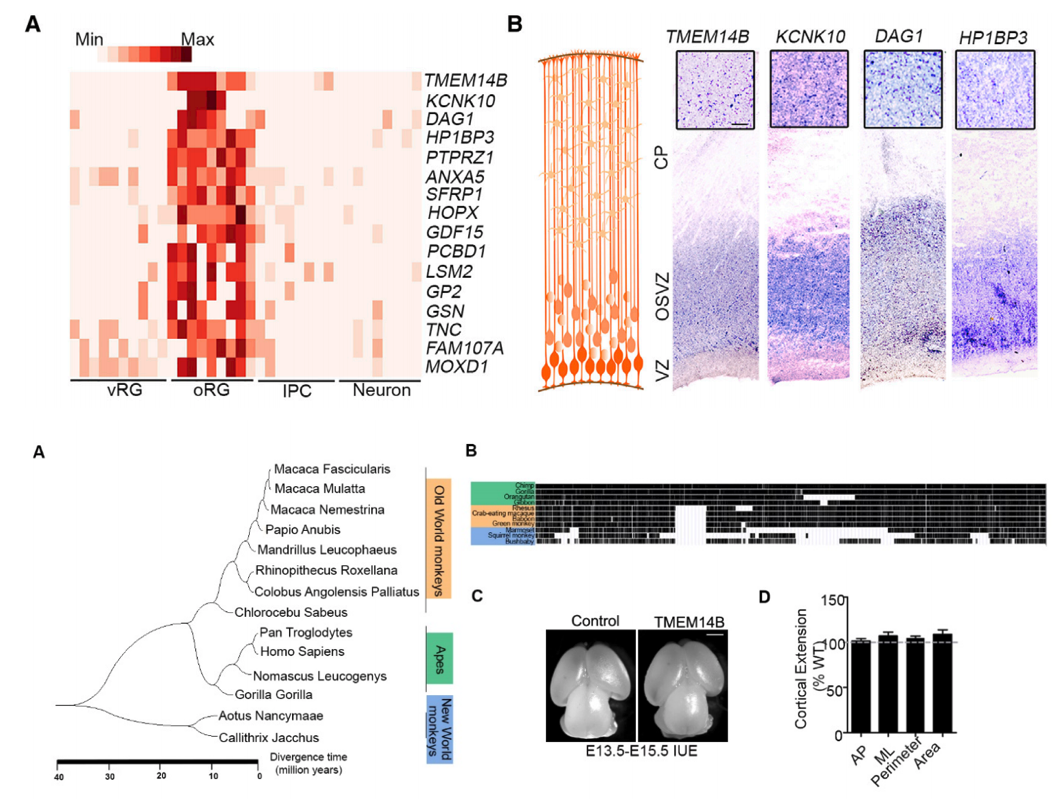
(1)神经前体细胞发育相关重要因子TMEM14B的发现
TMEM14B是灵长类动物特有基因,本人通过新开发的算法发掘出TMEM14B,并认为TMEM14B是oRG细胞的特异性基因。TMEM14B可以促进oRG细胞的快速扩增,从而促进皮层发育以及大脑沟回的形成。
(2)前列腺癌去势抵抗性形成重要相关基因的发现
去势抵抗前列腺癌具有高度致死性,而前列腺癌去势抵抗性的产生则由一系列重要因子引起,本人通过新开发的算法发现这个过程中起到重要作用的两个重要基因。这两个基因可以显著恶化去势抵抗前列腺癌预后,因此其抑制剂可以有效用于去势抵抗前列腺癌的治疗。
(3)转录组大数据整合算法ITRDR方法的开发
本人将机器学习中常用的蒙特卡洛算法用于转录组大数据的整合工作,并且根据转录组大数据的特点对算法进行一系列优化。新算法可以有效的整合不同来源的转录组大数据,并高效精确的筛选到研究对象的重要因子。实验验证表明,筛选到的因子有高概率具有生物学意义,因此证实ITRDR方法是有效的转录组大数据整合和筛选方法。
代表性论文:
(1) Jing Liu#, Wensu Liu#, Lu Yang#, Qian Wu#, Haofeng Zhang, Ai Fang, Long Li, Xiaohui Xu, Jun Zhang*, Fuchou Tang*&XiaoqunWang*. Primate-specific gene TMEM14B promotes cortical expansion and folding. cell stem cell, 2017 Nov 2; 21 (5): 635-649. e8. doi: 10. 1016/j. stem. 2017. 08. 013. Epub 2017 Oct 12
(2) Wensu Liu#, Ming Li#, Jing Qu*, Guang-Hui Liu*. Reevaluation of the safety of induced pluripotent stem cells: a call from somatic mosaicism. Protein&Cell , 4(2):83–85, 2013.
(3) Li M#, Liu WS#, Yuan T, Bai R, Liu GH*, Zhang W*, Qu J*. DNA methylome: Unveiling your biological age. Protein & cell, 4 (10 ):723-725, 2013.
(4) Kun Li , Wensu Liu#, Qian Zhao, Chunxia Wu , Chenxing Fan , Hong Lai, Shizheng Li*. Combination of Tanshinone IIA and doxorubicin possesses synergism and attenuation effects on doxorubicin in the treatment of breast cancer. Phytotherapy Research, 2019, Feb 5, 33:1658-1669. doi: 10.1002/ptr